- +1
河南农业大学陈震/姬祥团队:AI点亮基因组编辑的未来图景

生命科学 Life science
以CRISPR/Cas系统为主的基因组编辑技术已在基础研究、农业育种和生物医药等领域展现出巨大的应用潜力,然而如何高效发现、设计与改造新型基因组编辑工具仍是难以解决的领域瓶颈。河南农业大学农学院陈震与姬祥教授团队在Cell Press细胞出版社旗下期刊Trends in Biotechnology发表题为“AI sheds new light on genome editing”的综述。该研究系统综述了深度学习技术在基因组编辑领域中的应用与发展,从挖掘自然界隐藏的基因编辑工具,到定制超越自然的分子机器。深度学习已驱动CRISPR基因组编辑技术进入“智能”时代,并以三大颠覆性路径重塑生物技术边界。
有兴趣在Trends in Biotechnology发表您的综述或科研论文?请扫描提交论文提案 (presubmission form)。
AI掘金“暗物质”,发现新型基因组编辑器
AI助力新型基因编辑器的发现突破了传统序列比对的限制。传统序列比对工具如BLAST和HMMER在识别远缘同源蛋白时因序列差异大而效果受限,而深度学习结合“序列–结构–功能”范式,通过蛋白质三维结构的预测和分析,大幅提升了识别能力。随着AlphaFold DB等高质量结构数据库的开放,科学家们开展了大规模结构聚类和结构同源搜索,成功挖掘出多种新型Cas蛋白,包括新型碱基编辑蛋白、RNA引导的Cas13家族蛋白、TIGR-Tas和EphcCasλ等。
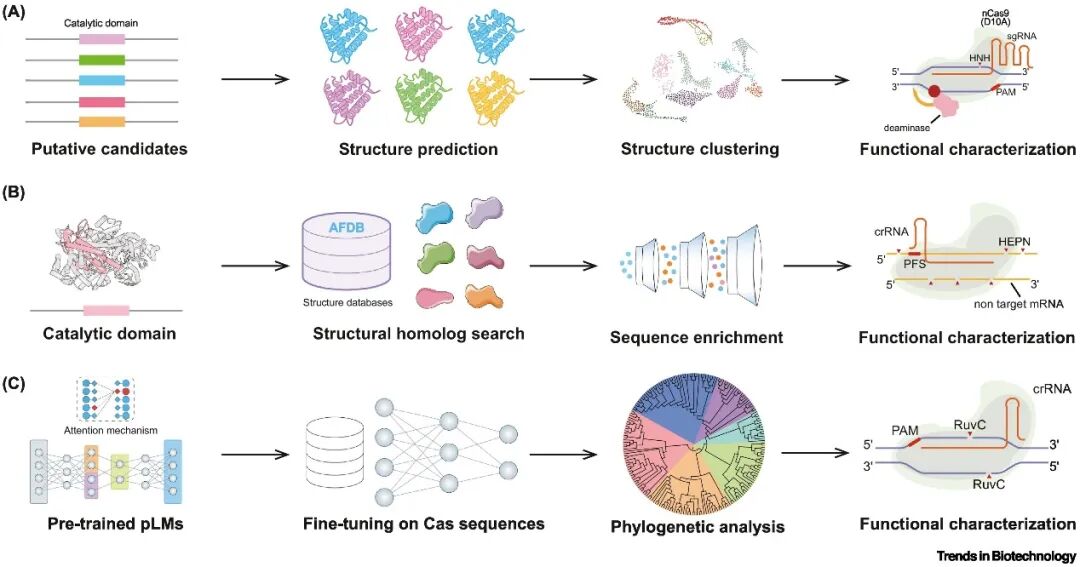
图1 人工智能辅助的基因编辑器深度挖掘
AI实现基因编辑蛋白的快速in silico进化
传统的高通量突变筛选和理性设计耗时费力,机器学习辅助的定向进化(MLDE)和零样本(Zero-shot)蛋白设计为这一难题提供了新的解决思路:即在实验数据不足时,直接用深度学习模型预测有益突变,大大降低了对实验筛选数据的依赖。零样本方法利用预训练模型预测有益突变,快速锁定潜在突变位点,而少样本方法结合少量实验数据与主动学习策略,可以显著提高突变的成功率。例如,结合结构信息的多模态深度模型ProMEP,进化出了效率提升多倍的TnpB和TadA变体,性能甚至超越实验室进化版ABE8e。
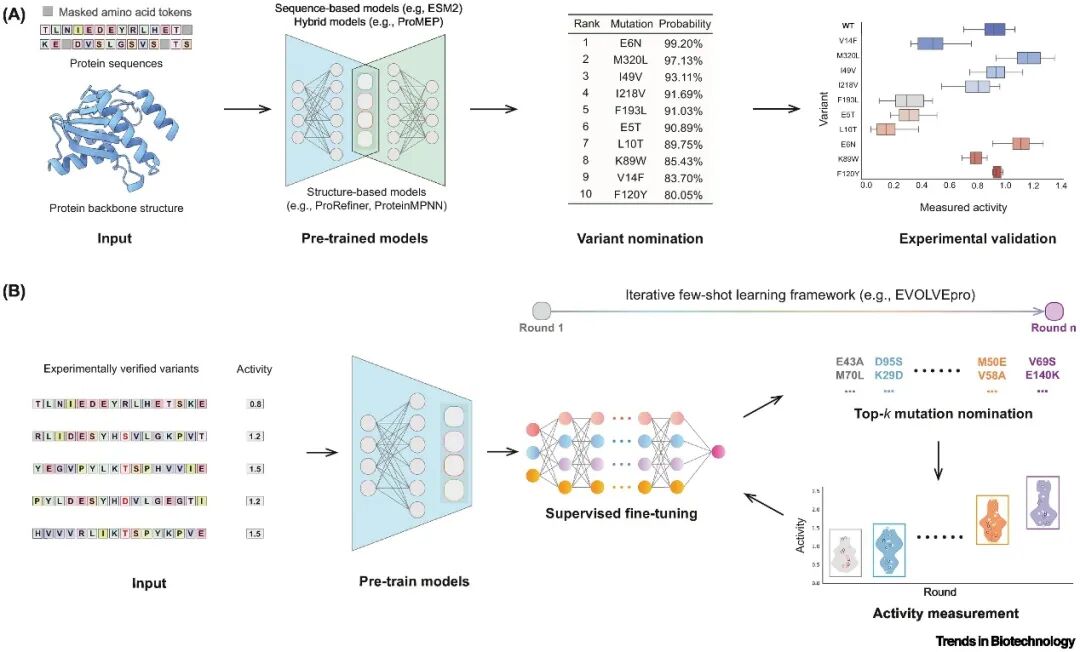
图2 基因编辑工具的高效改造
基因编辑工具的从头设计
深度生成式AI模型为基因编辑工具的从头设计开辟了新路径。大语言模型通过学习大量序列数据,能够设计出自然界尚不存在的全新基因编辑器,如Open-CRISPR-1和EvoCas9-1。扩散模型更能生成符合功能需求的三维蛋白结构,研究者们结合RFdiffusion、ProteinMPNN和AlphaFold,成功开发出高效的PE7-SB,在人类细胞中将引导编辑效率提高了近30倍。虽然目前多数设计案例仍处于初步验证阶段,但生成式AI展示了设计复杂“分子机器”的巨大潜力,为基因编辑技术的未来发展奠定了坚实基础。
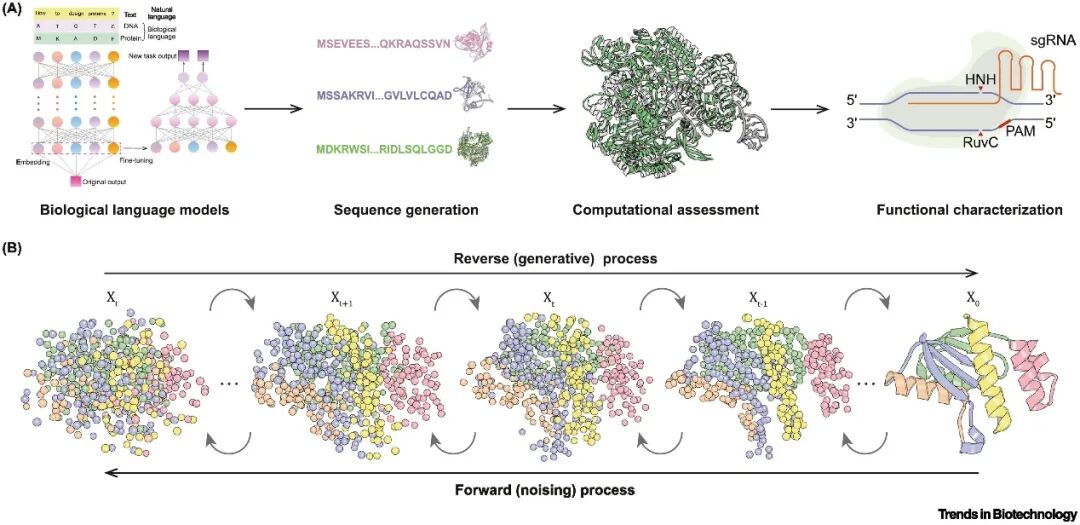
图3 基因编辑工具的从头设计
AI与生物技术的深度交叉无疑为科学研究和实际应用带来了前所未有的机遇。随着AI技术的持续发展,未来有望发现和设计出更多样化的基因编辑工具,深化对CRISPR进化机制的理解,推动基因编辑技术不断升级。
本文参考文献(上线划动查看)
1. Qin Z, Deng Z, Li C, Wang D, Ji X, Chen Z. AI sheds new light on genome editing. Trends Biotechnol. 2025 Jul 30:S0167-7799(25)00272-0. doi: 10.1016/j.tibtech.2025.07.011.
2. Moor, M. et al. (2023) Foundation models for generalist medical artificial intelligence. Nature 616, 259–265
3. Ferruz, N. et al. (2023) From sequence to function through struc-ture: deep learning for protein design. Comput. Struct. Biotechnol. J. 21, 238–250
4. Listov, D. et al. (2024) Opportunities and challenges in design and optimization of protein function. Nat. Rev. Mol. Cell Biol. 25, 639–653
5. Lau, A.M. et al. (2024) Exploring structural diversity across the protein universe with the encyclopedia of domains. Science 386, eadq4946
论文作者介绍
陈震
教授
陈震,河南农业大学特聘教授、博士生导师。2014年博士毕业于中国农业大学。主要从事生物信息学相关算法与软件开发工作,研究成果以第一作者或通讯作者发表在Nucleic Acids Research, Trends in Biotechnology, Briefings in Bioinformatics, Genomics, Proteomics &Bioinformatics等期刊,主持承担多项国家自然科学基金项目。

姬祥
教授
姬祥,河南农业大学教授,博士生导师。2019年博士毕业于中国科学院遗传与发育生物学研究所,2015-2016年在明尼苏达大学访问学习。主要从事作物基因组编辑技术开发及麦类作物优异性状改良的研究,研究成果以通讯或第一(共同第一)作者在Nature Biotechnology、Nature Plants、Trends in Biotechnology、Journal of Integrative Plant Biology等期刊发表,主持承担国家自然科学基金项目(面上、青年),国家重点研发计划子课题、河南省优青等项目。
▌论文标题:
AI sheds new light on genome editing
▌论文网址:
https://www.sciencedirect.com/science/article/abs/pii/S0167779925002720
▌DOI:
https://doi.org/10.1016/j.tibtech.2025.07.011
原标题:《河南农业大学陈震/姬祥团队Trends in Biotechnology综述 | AI点亮基因组编辑的未来图景》
本文为澎湃号作者或机构在澎湃新闻上传并发布,仅代表该作者或机构观点,不代表澎湃新闻的观点或立场,澎湃新闻仅提供信息发布平台。申请澎湃号请用电脑访问http://renzheng.thepaper.cn。





- 报料热线: 021-962866
- 报料邮箱: news@thepaper.cn
互联网新闻信息服务许可证:31120170006
增值电信业务经营许可证:沪B2-2017116
© 2014-2026 上海东方报业有限公司




